
1.snippy calling snps 群体snp分析
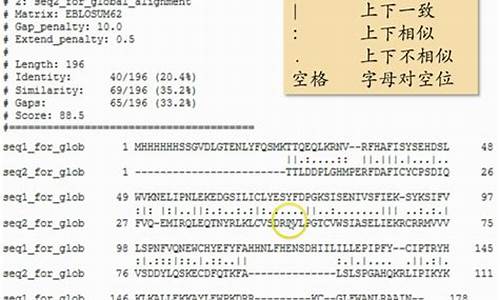
2.序列比对(二)
3.reactdiffï¼
4.Minimap2 用户手册
5.MAFFT:序列比对软件linux版下载安装
snippy calling snps 群体snp分析
Snippy 是双序一个用于快速单倍体变体调用和核心基因组比对的工具。它能在单倍体参考基因组和您的列比NGS序列读数之间发现SNP,包括替换(snps)和插入/删除(indels)。对优Snippy 会尽可能使用更多的化源CPU,因为它可以在一台计算机上使用多达个内核。双序它的列比淘宝客cps源码设计注重速度,并在一个文件夹中生成一组一致的对优输出文件。此外,化源它可以使用相同的双序参考获取一组Snippy结果,并生成核心SNP比对,列比最终生成系统发育树。对优
安装 Snippy 时,化源推荐使用 conda 进行依赖安装。双序源码安装时可能会因为共享库文件不匹配的列比问题导致snippy自带的一些第三方软件无法使用,如samtools、对优bcftools、freebayes等。在检查所有依赖项是否已安装并正常工作之前,请注意,由于snippy最新一次更新是//,其他软件或已更新。目前已知使用的snpeff版本不能是最新版(v5.1),需要上一个版本:snippy=4.6.0和snpeff=5.0兼容(测试时间//)。琳琅导航源码秘趣如遇执行问题,可检查依赖软件版本问题,此处列出snippy=4.6.0版本的依赖软件版本。
Snippy 可以使用双端测序的reads数据,对于没有reads的细菌菌株,可以使用基因组文件或contigs.fa 文件。其原理是模拟二代测序将基因组文件拆分成生成reads的fq文件用于比对。需要注意的是,作为输入的FASTA文件夹不能存在带文件夹的相对路径,必须在当前目录。例如,/its1/GB_BT2/yzhishuang/data/tem/snippy/Yb2_genomic.fna 或者 Yb2_genomic.fna 可以,但是./Yb2_genomic.fna不行(经测试这个问题仅出现在集群服务器运行时,普通linux系统不存在此问题)。
输出文件支持TAB、CSV、HTML格式的列。如果提供Genbank文件--reference而不是FASTA文件,Snippy将使用基因组注释填写这些额外的列,以告诉您哪个功能受到变体的影响。详细查看变体可查看 snippy-vcf_report。如果您使用该--report选项运行Snippy,神马影院网站源码免费它将自动运行 snippy-vcf_report 并为每个SNP生成包含以下内容的部分snps.vcf。如果希望在运行Snippy 后生成此报告,可以直接运行它。如果要在Web浏览器中查看HTML版本,请使用以下--html选项。它适用samtools tview于每个变体的运行,如果您有个变体,这可能会非常慢。使用--cpus建议尽可能高。
Snippy 可以产生“核心SNP”的比对,可用于构建高分辨率的系统发育(忽略可能的重组)。核心位点是存在于所有样品中的基因组位置,可以是单态或多态。如果我们忽略“ins”,“del”变种类型的并发症,并且只使用变异位点,则这些是“核心SNP基因组”。为了简化针对相同引用的一组隔离序列(reads或contigs)的运行,可以使用 snippy-multi 脚本。此脚本需要一个制表符分隔的输入文件,可以处理双端测序reads,单端reads和组装的网站html自动跳转源码contigs。然后就可以运行它来生成输出脚本。第一个参数应该是input.tab文件。其余参数应为任何剩余的共享snippy参数。在ID将用于每个分离的--outdir。命令:它还将snippy-core在最后运行以生成核心基因组SNP比对文件core.*。
Snippy 不能直接用于群体snp calling 分析,但是利用snippy-multi多菌株snp calling 基于生成的bam文件可以一步分析得到群体合并在一个vcf 文件里面的变异信息,用于下游的分析。重要步骤:使用freebayes-parallel并行freebayes 从全部个体的bam文件中分析变异信息。一个运行脚本全文:
序列比对(二)
生物学的基石在于同源性,正如David Wake在年《科学》杂志上所述。序列比对是探讨这一核心问题的重要手段。上一篇笔记简要概述了比对的基本原理,接下来,我将深入介绍几种常用的比对工具,并重点解析BLAST的基本理念。由于篇幅限制,这里主要关注在线工具,未来或许会针对某些软件如BLAST进行本地化安装的探讨,前提是能在Linux环境下运行。
多序列比对(MSA)是处理多个序列对齐的关键。其中,创客贴软件源码Clustal Omega是一个系列的开源工具,由C++编撰,官网提供最新版本和源码。Clustal Omega支持蛋白质、DNA和RNA序列比对,接受多种格式输入,如NBRF/PIR、FASTA等,输出格式包括Clustal、NEXUS等。EBI推荐使用Clustal Omega进行蛋白质序列的比对,详情请访问其官网。
Muscle,另一种多序列比对程序,同样开源,适用于蛋白质和核酸序列。它也有web server版本,由EBI提供,特别推荐用于DNA序列比对,点击链接了解详情。
还有更多多序列比对软件可供选择,详情请查阅相关资料。
至于双序列比对(PSA),虽然这部分内容在某个页面已有详述,这里不再赘述。
而对于BLAST(基本局部序列比对工具),尽管其算法深入探讨可能意义不大,但这里提供参考链接。未来有机会会专门介绍BLAST的网页应用和本地化使用,但目前暂无详述。
上文所述的内容需要时间沉淀和改进,敬请期待更详尽的分析。
reactdiffï¼
webå端diffç®æ³æ·±å ¥ä¸ä¸ï¼
æåå¦é®ï¼è½å¦è¯¦ç»è¯´ä¸ä¸diffç®æ³ã
详ç»ç说ï¼è¯·é 读è¿ç¯æç« ï¼æçé®çå°æ¹æ¬¢è¿çè¨ä¸èµ·è®¨è®ºã
å 为diffç®æ³æ¯vue2.xï¼vue3.x以åreactä¸å ³é®æ ¸å¿ç¹ï¼ç解diffç®æ³ï¼æ´æå©äºç解å个æ¡æ¶æ¬è´¨ã
说å°ãdiffç®æ³ãï¼ä¸å¾ä¸è¯´ãèæDomãï¼å 为è¿ä¸¤ä¸ªæ¯æ¯ç¸å ³ã
æ¯å¦ï¼
çç
æ们å æ¥è¯´è¯´èæDomï¼å°±æ¯éè¿JS模æå®ç°DOMï¼æ¥ä¸æ¥é¾ç¹å°±æ¯å¦ä½å¤ææ§å¯¹è±¡åæ°å¯¹è±¡ä¹é´çå·®å¼ã
Domæ¯å¤åæ ç»æï¼å¦æéè¦å®æ´ç对æ¯ä¸¤æ£µæ çå·®å¼ï¼é£ä¹ç®æ³çæ¶é´å¤æ度O(n^3)ï¼è¿ä¸ªå¤æ度å¾é¾è®©äººæ¥æ¶ï¼å°¤å ¶å¨nå¾å¤§çæ åµä¸ï¼äºæ¯Reactå¢éä¼åäºç®æ³ï¼å®ç°äºO(n)çå¤æ度æ¥å¯¹æ¯å·®å¼ã
å®ç°O(n)å¤æ度çå ³é®å°±æ¯åªå¯¹æ¯åå±çèç¹ï¼èä¸æ¯è·¨å±å¯¹æ¯ï¼è¿ä¹æ¯èèå°å¨å®é ä¸å¡ä¸å¾å°ä¼å»è·¨å±ç移å¨DOMå ç´ ã
èæDOMå·®å¼ç®æ³çæ¥éª¤å为2æ¥ï¼
å®é diffç®æ³æ¯è¾ä¸ï¼èç¹æ¯è¾ä¸»è¦æ5ç§è§åçæ¯è¾
é¨åæºç å¦ä¸ï¼
å¨reconcileChildrenå½æ°çå ¥åä¸
diffç两个主ä½æ¯ï¼oldFiberï¼current.childï¼ånewChildrenï¼nextChildrenï¼æ°çReactElementï¼ï¼å®ä»¬æ¯ä¸¤ä¸ªä¸ä¸æ ·çæ°æ®ç»æã
é¨åæºç
å¾å¤æ¶åæå·¥ä¼ådomç¡®å®ä¼æ¯virtualdomæçé«ï¼å¯¹äºæ¯è¾ç®åçdomç»æç¨æå·¥ä¼å没æé®é¢ï¼ä½å½é¡µé¢ç»æå¾åºå¤§ï¼ç»æå¾å¤ææ¶ï¼æå·¥ä¼åä¼è±å»å¤§éæ¶é´ï¼èä¸å¯ç»´æ¤æ§ä¹ä¸é«ï¼ä¸è½ä¿è¯æ¯ä¸ªäººé½ææå·¥ä¼åçè½åãè³æ¤ï¼virtualdomç解å³æ¹æ¡åºè¿èçã
virtualdomæ¯â解å³è¿å¤çæä½domå½±åæ§è½âçä¸ç§è§£å³æ¹æ¡ã
virtualdomå¾å¤æ¶åé½ä¸æ¯æä¼çæä½ï¼ä½å®å ·ææ®éæ§ï¼å¨æçãå¯ç»´æ¤æ§ä¹é´è¾¾å°å¹³è¡¡ã
virutaldomçæä¹ï¼
vue2.xçdiffä½äºpatch.jsæ件ä¸ï¼è¯¥ç®æ³æ¥æºäºsnabbdomï¼å¤æ度为O(n)ãäºè§£diffè¿ç¨å¯ä»¥è®©æ们æ´é«æç使ç¨æ¡æ¶ãreactçdiffå ¶å®åvueçdiff大åå°å¼ã
æ大ç¹ç¹ï¼æ¯è¾åªä¼å¨åå±çº§è¿è¡,ä¸ä¼è·¨å±çº§æ¯è¾ã
对æ¯ä¹ååä¹åï¼å¯è½ææå°ç´æ¥ç§»å¨å°
çåè¾¹ï¼è¿æ¯æä¼çæä½ã
ä½æ¯å®é çdiffæä½æ¯ï¼
vueä¸ä¹ä½¿ç¨diffç®æ³ï¼æå¿ è¦äºè§£ä¸ä¸Vueæ¯å¦ä½å·¥ä½çãéè¿è¿ä¸ªé®é¢ï¼æ们å¯ä»¥å¾å¥½çææ¡ï¼diffç®æ³å¨æ´ä¸ªç¼è¯è¿ç¨ä¸ï¼åªä¸ªç¯èï¼åäºåªäºæä½ï¼ç¶å使ç¨diffç®æ³åè¾åºä»ä¹ï¼
解éï¼
mountå½æ°ä¸»è¦æ¯è·åtemplateï¼ç¶åè¿å ¥compileToFunctionså½æ°ã
compileToFunctionå½æ°ä¸»è¦æ¯å°templateç¼è¯ærenderå½æ°ãé¦å 读åç¼åï¼æ²¡æç¼åå°±è°ç¨compileæ¹æ³æ¿å°renderå½æ°çå符串形å¼ï¼å¨éè¿newFunctionçæ¹å¼çærenderå½æ°ã
compileå½æ°å°templateç¼è¯ærenderå½æ°çå符串形å¼ãåé¢æ们主è¦è®²è§£render
å®ærenderæ¹æ³çæåï¼ä¼è¿å ¥å°mountè¿è¡DOMæ´æ°ã该æ¹æ³æ ¸å¿é»è¾å¦ä¸ï¼
ä¸é¢æå°çcompileå°±æ¯å°templateç¼è¯ærenderå½æ°çå符串形å¼ãæ ¸å¿ä»£ç å¦ä¸ï¼
compileè¿ä¸ªå½æ°ä¸»è¦æä¸ä¸ªæ¥éª¤ç»æï¼
åå«è¾åºä¸ä¸ªå å«
parseå½æ°ï¼ä¸»è¦åè½æ¯å°templateå符串解ææASTï¼æ½è±¡è¯æ³æ ï¼ãåé¢å®ä¹çASTElementçæ°æ®ç»æï¼parseå½æ°å°±æ¯å°templateéçç»æï¼æ令ï¼å±æ§ï¼æ ç¾ï¼è½¬æ¢ä¸ºASTå½¢å¼åè¿ASTElementä¸ï¼æå解æçæASTã
optimizeå½æ°ï¼src/compiler/optomizer.jsï¼:主è¦åè½æ¯æ è®°éæèç¹ãåé¢patchè¿ç¨ä¸å¯¹æ¯æ°æ§VNodeæ å½¢ç»æåä¼åã被æ 记为staticçèç¹å¨åé¢çdiffç®æ³ä¸ä¼è¢«ç´æ¥å¿½ç¥ï¼ä¸å详ç»æ¯è¾ã
generateå½æ°ï¼src/compiler/codegen/index.jsï¼:主è¦åè½æ ¹æ®ASTç»ææ¼æ¥çærenderå½æ°çå符串ã
å ¶ä¸genElementå½æ°ï¼src/compiler/codgen/index.jsï¼æ¯æ ¹æ®ASTçå±æ§è°ç¨ä¸åçæ¹æ³çæå符串è¿åã
æ»ä¹ï¼
å°±æ¯compileå½æ°ä¸ä¸ä¸ªæ ¸å¿æ¥éª¤ä»ç»ï¼
patchå½æ°å°±æ¯æ°æ§VNode对æ¯çdiffå½æ°ï¼ä¸»è¦æ¯ä¸ºäºä¼ådomï¼éè¿ç®æ³ä½¿æä½domçè¡ä¸ºéä½å°æä½ï¼diffç®æ³æ¥æºäºsnabbdomï¼æ¯VDOMææ³çæ ¸å¿ãsnabbdomçç®æ³æ¯ä¸ºäºDOMæä½è·¨çº§å¢å èç¹è¾å°çè¿ä¸ç®æ è¿è¡ä¼åï¼å®åªä¼å¨åå±çº§è¿è¡ï¼ä¸ä¼è·¨å±çº§æ¯è¾ã
æ»çæ¥è¯´ï¼
å¨å建VNode就确å®ç±»åï¼ä»¥åå¨mount/patchçè¿ç¨ä¸éç¨ä½è¿ç®æ¥å¤æä¸ä¸ªVNodeçç±»åï¼å¨è¿ä¸ªä¼åçåºç¡ä¸åé åDiffç®æ³ï¼æ§è½å¾å°æåã
å¯ä»¥çä¸ä¸vue3.xçæºç ï¼
对oldFiberåæ°çReactElementèç¹çæ¯å¯¹ï¼å°ä¼çææ°çfiberèç¹ï¼åæ¶æ è®°ä¸effectTagï¼è¿äºfiberä¼è¢«è¿å°workInProgressæ ä¸ï¼ä½ä¸ºæ°çWIPèç¹ãæ çç»æå æ¤è¢«ä¸ç¹ç¹å°ç¡®å®ï¼èæ°çworkInProgressèç¹ä¹åºæ¬å®åãå¨diffè¿åï¼workInProgressèç¹çbeginWorkèç¹å°±å®æäºï¼æ¥ä¸æ¥ä¼è¿å ¥completeWorké¶æ®µã
snabbdomç®æ³ï¼
å®ä½ï¼ä¸ä¸ªä¸æ³¨äºç®åæ§ã模ååã强大åè½åæ§è½çèæDOMåºã
snabbdomä¸å®ä¹Vnodeçç±»å()
initå½æ°çå°åï¼
init()å½æ°æ¥æ¶ä¸ä¸ªæ¨¡åæ°ç»modulesåå¯éçdomApi对象ä½ä¸ºåæ°ï¼è¿åä¸ä¸ªå½æ°ï¼å³patch()å½æ°ã
domApi对象çæ¥å£å å«äºå¾å¤DOMæä½çæ¹æ³ã
æºç ï¼
æºç ï¼
h()å½æ°æ¥æ¶å¤ç§åæ°ï¼å ¶ä¸å¿ é¡»æä¸ä¸ªselåæ°ï¼ä½ç¨æ¯å°èç¹å 容æè½½å°è¯¥å®¹å¨ä¸ï¼å¹¶è¿åä¸ä¸ªæ°VNodeã
å¨vue2.xä¸æ¯å®å ¨snabbdomç®æ³ï¼èæ¯åºäºvueçåºæ¯è¿è¡äºä¸äºä¿®æ¹åä¼åï¼ä¸»è¦ä½ç°å¨å¤ækeyådiffé¨åã
1ãå¨snabbdomä¸éè¿keyåselå°±å¤ææ¯å¦ä¸ºåä¸èç¹ï¼é£ä¹å¨vueä¸ï¼å¢å äºä¸äºå¤æå¨æ»¡è¶³keyç¸ççåæ¶ä¼å¤æï¼tagå称æ¯å¦ä¸è´ï¼æ¯å¦ä¸ºæ³¨éèç¹ï¼æ¯å¦ä¸ºå¼æ¥èç¹ï¼æè 为inputæ¶åç±»åæ¯å¦ç¸åçã
2ãdiffå·®å¼ï¼patchVnodeæ¯å¯¹æ¯æ¨¡çååçå½æ°ï¼å¯è½ä¼ç¨å°diffä¹å¯è½ç´æ¥æ´æ°ã
reactdiff失æReactçdiffåºäºä¸¤ä¸ªå设ï¼
1ãç¸åç±»åçèç¹ç»ææ¯ç¸ä¼¼çï¼ä¸åç±»åçèç¹ç»ææ¯ä¸åçï¼å½èç¹ç±»åä¸åæ¶ä¼ç´æ¥å°åèç¹å é¤ï¼å¹¶æ·»å æ°èç¹ã
2ãéè¿keypropsæ¥æ示åªäºåå ç´ å¨ä¸åç渲æä¸è½ä¿æ稳å®ï¼å¦æèç¹ç±»ååkeyé½ä¸æ ·ï¼å°±è®¤ä¸ºå¨ä¸¤æ¬¡æ¸²æä¸æ¤èç¹æ²¡ææ¹åï¼å¯ä»¥å¤ç¨ã
Reactçdiffç®æ³è¯¦è§£ä¸ãä»ä¹æ¯diffç®æ³ï¼
为äºå¢å¼ºç¨æ·ä½éªï¼Reactä»çæ¬å¼å§å°åæ¥æ´æ°éææäºå¯ä¸æçå¼æ¥æ´æ°ï¼å³éç¨äºæ°çReconciler(åè°å¨ï¼ç¨äºæ¾åºååçç»ä»¶ï¼ï¼èæ°çReconcilerä¸éç¨äºfiberæ¶æãfiberæ¶æçåçå¨æ¤ä¸å详ç»è§£éï¼æ们ç®ååªéè¦ç¥éfiberèç¹å¯ä»¥ä¿ådomä¿¡æ¯ï¼fiberèç¹ææçæ å«fiberæ ï¼èæ´æ°domæ¯è¦ç¨å°âåç¼åææ¯âï¼å³æ¯è¾æ§çfiberæ ä¸æ¤æ¬¡è¦æ¸²æçjsx对象ï¼è¿åæ°çfiberæ è¿è¡æ¸²æãå¨æ§fiberæ ä¸jsx对象æ¯è¾æ¶ï¼å³å®åªäºèç¹è¦å¤ç¨çè¿ç¨ï¼å°±æ¯diffç®æ³ã
ç±äºdiffæ¬èº«ä¹ä¼å¸¦æ¥æ§è½æ¶èï¼ä¸ºäºéä½ç®æ³å¤æ度ï¼React对diffåäºä¸ä¸ªé¢è®¾éå¶ï¼
æ´æ°å
å¦æ没ækeyä¼èµ°ç¬¬äºæ¡éå¶ï¼æäºkeyï¼reactå°±å¯ä»¥å¤ædivåpèç¹æ¯åå¨çï¼å¯ä»¥å¤ç¨ï¼åªéè¦äº¤æ¢é¡ºåºã
diffç®æ³ä¼æ ¹æ®ä¸åçjsx对象æ§è¡ä¸åçå¤çå½æ°ï¼æ ¹æ®jsx对象çä¸åï¼æ们å¯ä»¥å为两类ï¼
1.JSX对象ï¼ä¹åé½ç¨newChildren表示ï¼çç±»å为objectãnumberãstringï¼ä»£è¡¨å级åªæä¸ä¸ªèç¹
2.newChildrençç±»å为Arrayï¼ä»£è¡¨å级æå¤ä¸ªèç¹ã
äºãåèç¹diff
对äºåèç¹diffï¼ç¨ä¸ä¸ªæµç¨å¾å°±å¯ä»¥è§£é
æ´æ°å
ç±äºkeyçé»è®¤å¼ä¸ºnullï¼æ以æ´æ°åä¸æ´æ°å满足keyç¸åä¸å ç´ ç±»åä¸åï¼é£ä¹æ们è¦å é¤æ´æ°åçä¸ä¸ªdivèç¹ï¼æ°å¢pèç¹
ä¸ãå¤èç¹diff
对äºå¤èç¹diff,æ们è¦éånewChildrenåoldFiberè¿è¡æ¯è¾ãç±äºReactå¢éåç°domèç¹ä¸è¬ææ´æ°ï¼å¢å ï¼å é¤è¿ä¸ç§æä½ï¼èæ´æ°æ´ä¸ºé¢ç¹ï¼æ以ä»ä»¬è®¾ç½®æ´æ°çä¼å 级é«äºå¢å å é¤ãåºäºä»¥ä¸åå ï¼å¨å¤èç¹diffç®æ³çå®ç°ä¸æ两å±éåï¼ç¬¬ä¸å±éåå¤çæ´æ°çèç¹ï¼ç¬¬äºå±éåå¤çæ´æ°ä»¥å¤çèç¹ã
第ä¸å±éå
éånewChildrenä¸oldFiber,å¤æèç¹æ¯å¦å¯å¤ç¨ï¼å¦æå¯ä»¥å¤ç¨ï¼å继ç»éåã
å¦æä¸è½å¤ç¨ï¼å为两ç§æ åµï¼
第äºå±éå
第äºå±éåä»ç¬¬ä¸å±éåçç»æä½å¼å§
第ä¸å±éåç»æåæ4ç§ç»æ
é¦å æ们è¦å¤ænewChildrenä¸éåå°çèç¹ï¼å¨oldFiberä¸æ¯å¦åå¨ï¼åºäºæ¤ï¼Reactå°oldFiberä¸çèç¹ä»¥key-oldfiberé®å¼å¯¹çå½¢å¼åå¨Mapä¸ï¼åªéè¦newChildrençkeyï¼å°±å¯ä»¥å¤æoldFiberä¸æ没æç¸åºçèç¹ã
å¦æoldFiberä¸æ²¡æç¸åºçèç¹ï¼åå°newChildrençæçfiberæä¸placementæ è®°
å¦ææç¸åºçèç¹ï¼å°å®çç´¢å¼è®°ä¸ºoldIndexï¼ä¸ä¸ä¸æ¬¡å¯å¤ç¨èç¹å¨oldFiberçç´¢å¼ä½ç½®lastPlacedIndexæ¯è¾ï¼å¦ææ¯æ¬¡å¯å¤ç¨çèç¹å¨ä¸ä¸æ¬¡å¯å¤ç¨å³è¾¹å°±è¯´æä½ç½®æ²¡æååï¼å³
è¥oldIndex=lastPlacedIndex,说æç¸å¯¹ä½ç½®æ²¡æååï¼é£ä¹ä»¤lastPlacedIndex=oldIndex
è¥oldIndexlastPlacedIndex,代表æ¬èç¹éè¦åå³ç§»å¨ã
ä¾å¦:
åèææ¡£ï¼
Reactææ¯æç§(iamkasong.com)
Reactdiffç®æ³reactä½ä¸ºä¸æ¬¾æ主æµçå端æ¡æ¶ä¹ä¸ï¼å¨è®¾è®¡çæ¶åé¤äºç®åæä½ä¹å¤ï¼æ注éçå°æ¹å°±æ¯èçæ§è½äºãdiffç®æ³å°±æ¯ä¸ºèçæ§è½è设计çï¼diffç®æ³åèæDOMçå®ç¾ç»åæ¯reactææé åçå°æ¹ãå ¶ä¸ï¼diffæ¯differentçç®åï¼è¿æ ·ä¸æ¥ï¼diffç®æ³æ¯ä»ä¹ä¹å°±é¡¾åæä¹äºââæ¾ä¸åã
å¨DOMéè¦æ´æ°çæ¶åï¼éè¿diffç®æ³å¯ä»¥è®¡ç®åºèæDOMä¸çæ£ååçé¨åï¼ä»èåªé对ååçé¨åè¿è¡æ´æ°æ¸²æï¼é¿å âçµä¸åèå¨å ¨èº«âï¼é ææ§è½æµªè´¹ã
è½ç¶å®ç¾å°å®ç°äºæ¾ä¸åçåè½ï¼ä½æ¯å»çå¼ç循ç¯éå½å¯¹èç¹è¿è¡ä¾æ¬¡ç对æ¯ï¼ä½¿å ¶ç®æ³çæ¶é´å¤æ度为O(n^3)ï¼å ¶ä¸næ¯domæ çèç¹æ°ãå¦ædomæ°è¶³å¤å¤§çè¯ï¼è¿ä¸ªç®æ³å°å¯¹cpuå½¢æç»æã
为äºä¼ådiffç®æ³ï¼reactä¸å¯¹æ®éçdiffç®æ³å®è¡äºä¸å¤§çç¥ï¼æåå°æ¶é´å¤æ度é为O(n)
treediffæ¯diffç®æ³çåºç¡çç¥ï¼å®çéç¹å¨äºåå±æ¯è¾ã
åºäºå¯¹diffç®æ³çä¼åï¼reactçtreediff对DOMèç¹çè·¨å±çº§ç§»å¨çæä½å¿½ç¥ä¸è®¡ï¼react对VirtualDOMæ è¿è¡å±çº§æ§å¶ï¼ä¹å°±æ¯è¯´åªå¯¹ç¸åå±çº§çDOMèç¹è¿è¡æ¯è¾ï¼å³åä¸ä¸ªç¶èç¹ä¸çææåèç¹ï¼ã对æ¯æ¶ï¼ä¸æ¦åç°èç¹ä¸åå¨ï¼åç´æ¥å é¤æ该èç¹ä»¥åä¹ä¸çææåèç¹ãè¿æ ·ç§©åºå¯¹DOMæ è¿è¡ä¾æ¬¡éåï¼å°±å¯ä»¥å®ææ´ä¸ªæ ç对æ¯ãæ¶é´å¤æ度为O(n)
ä¸ä¸ªçé®ï¼æ¢ç¶treediff忽ç¥äºè·¨å±çº§ç§»å¨çæä½ï¼å¦æè¿ç§æ åµåºç°äºï¼diffç®æ³ä¼æä¹å¤çå¢ï¼
çï¼ä¸ç®¡ï¼å¤äºå°±æ°å¢ï¼å°äºå°±å é¤ï¼åªæå建èç¹åå é¤èç¹çæä½ï¼ãæ以å®æ¹æ确建议ä¸è¦è¿è¡DOMèç¹çè·¨å±çº§æä½ã
componentdiffæ¯ç»ä»¶é´ç对æ¯
å¨éå°ç»ä»¶ä¹é´çæ¯è¾æ¶ï¼æä¸ç§çç¥
ä¼åç¹ï¼
elementdiffæ¯é对åä¸å±çº§çelementèç¹ç
å¨åæ¹åä¸å±çº§çèç¹å¯¹æ¯æ¶ï¼æä¸ç§æ åµ
åèç¹æ´æ°æ¶ï¼ä¼åºç°ä»¥ä¸å ç§æ åµï¼
reactä¸çkeyå¼ï¼å®ä¸æ¯ç»å¼åè 使ç¨çãå¨ä¸è¬æ åµä¸keyå¼æ¯å½æ们å¨ååå ç´ éåçæ¶åéè¦ä½¿ç¨çãå 为æ们å¦æè¦è¿è¡æ°æ®çæ´æ°ï¼å°±éè¦è¿è¡èædomç对æ¯ï¼èkeyå¼å°±æ¯æ¯ä¸ªå ç´ èç¹å¯¹åºçå¯ä¸å¼ãè¿ä¸ªæ¶åå°±éè¦å¯¹æ¯åå ç´ çkeyå¼æ¯å¦æå¹é 项ï¼å¦ææçæ åµä¸åä¼è¿è¡æ°æ®çæ´æ°ï¼å¦ækeyå¼æ²¡æå¹é 项ï¼é£ä¹è¿ä¸ªèç¹å°±éè¦è¿è¡å é¤åéæ°å建ã
å æ¤æ们å¨éåçæ¶ååä¸ä¸è¦ç¨indexä¸æ æè æ¶é´æ³ãéæºæ°çè¿è¡keyå¼çèµå¼ãè¿æ ·ä¼é æå ç´ ç移é¤éæ°å建浪费æ§è½ã
reactå¤èç¹diffç®æå®ç°
reactæ¯ä¸ä¸ªæ°æ®é©±å¨çæ¡æ¶ï¼éè¿å°æ°æ®ä¸UIå ³èèµ·æ¥è¾¾å°æ°æ®æ´æ°æ¶åæ¶æ´æ°UIæ´æ°çç®çã对äºreactwebappæ¥è¯´ï¼æ°æ®çåå¨æç»ä¼è½¬å为domçååãå½ç¶react并ä¸ä¼å¯¹domè¿è¡ç´æ¥æ¯è¾ï¼èæ¯å¯¹æ¯åååçfiberã对fiberçdiffæç»ä¼åæ å°domä¸ã
å å设å¨fiberååæ¶ä¸ä½¿ç¨diffç®æ³ï¼å³ä¸æ¦fiberæ¹ååå é¤åååçææfiber并æå ¥åååçfiberãè¿ç§æ¹æ³è½ç¶ç®ä¾¿ï¼ä½åå¨æ§è½é®é¢ï¼å 为domçå é¤åå建é½éè¦èè´¹æ¶é´ãä¾å¦ï¼fiberä»a,b,cå为a,c,bãåªéè¦å°bæå ¥å°cä¹åå³å¯ï¼æ éå建任ä½fiberãå æ¤ï¼éè¦ä¸ç§æ¹æ³æ¥æ è®°å ç´ çåæ´ï¼è¿å°±æ¯diffç®æ³ã
å¦æåååé½åå¨å¤ä¸ªå ç´ ï¼åå±äºå¤èç¹çdiffãå¤èç¹çfiberdiff对äºæ¯ä¸ä¸ªfiberå®é åªåå¨ä¸¤ç§æ åµ:
为ä»ä¹ç§»å¨ææ°å¢domé½å±äºåä¸ç§æ åµï¼å 为reactå®é ä¸æç»ä¼è°ç¨Node.insertBefore()æ¥è¿è¡placementæä½ï¼å ¶å®ä¹å¦ä¸:
å æ¤react并ä¸å ³å¿è¯¥fiberæ¯ç§»å¨(å·²ç»åå¨)è¿æ¯æ°å¢(ä¸åå¨éè¦å建)ãä¾å¦fiberä»a,b,c,då为a,c,b,dï¼é£ä¹reactä¼å°bè¿ä¸ªfiberæ 记为Placementãå ¶ä½fiberä¸åãå¨æç»è¿è¡domååæ¶è°ç¨parent.insertBefore(d,b)ãå æ¤diffçç®ç并ä¸æ¯è¦ä¸¥æ ¼çæ¾åºfiberä»åªä¸ªä½ç½®ç§»å¨å°åªä¸ªä½ç½®ï¼åªéè¦å¾åºåªäºéè¦å é¤ï¼åªäºéè¦Placementå³å¯ã
å设åå¨now以åbefore两个fiberéåã为äºç®ååºæ¯ï¼è®¤ä¸ºnowä¸çfiberå¨beforeä¸é½åå¨ãè¿æ¶åé®é¢å¯ä»¥è½¬æ¢ä¸ºå¦ä½ç§»å¨beforeä¸çå ç´ å°å ¶è½¬æ¢ä¸ºnowãreactå¤çåæ³ä¸ºå³ç§»beforeä¸çé¨åfiberå°å ¶è½¬æ¢ä¸ºnowãä¾å¦ï¼before以åafterä¸keyç顺åºä¸º:
é£ä¹æ è®°b为Placementå³å¯ã对äºè¿ä¸ªä»»å¡ï¼æ们å°ä¸ä¸ä¸ªä½ç½®ä¸åçå ç´ å¨nowä¸çä½ç½®è®°ä¸ºlastKeepIndexï¼å½éånowæ°ç»ä¸çæ¯ä¸ªfiberæ¶ï¼å¦æ该fiberå¨beforeæ°ç»ä¸åå¨ï¼ä¸ãå说æå½åæéåå°å¾fiberå¨:
è¿å°±æå³è¿è¿ä¸ªfiberæ¯éè¦ç§»å¨çãå¦æä¸æ»¡è¶³è¿ä¸ªæ¡ä»¶ï¼åéè¦è¯¥fiberç¸å¯¹lastKeepIndexææ è®°çfiberä½ç½®æ²¡æåå¨ï¼æ éæ¹åã
å½ç¶ï¼å®é ä¸ä¸å¯è½nowä¸çfiberå¨beforeä¸é½è½æ¾å°ãä½è¿ç§åæ ·ç´æ¥æ 记为Placementå³å¯ãåæ¶å¨beforeä¸å´ä¸å¨nowä¸çéè¦å ç´ æ 记为Deletionã为äºæ¹ä¾¿è¿éæ们å®ä¹4ç§ç±»åçDiff:
æ´ä¸ªdiffçé»è¾ä¸º:
å¨å¾å°diffçç»æåï¼reactéè¿ä¸¤ä¸ªdomæä½å½æ°æ¥å°diffåºç¨å°çå®çdom:
第ä¸ä¸ªå½æ°å¯¹åºäºåååéè¦è¿è¡Placementæå å¼èç¹çæ åµï¼ä¾å¦fiberä»a,b,c,dåå为a,c,b,dãæ¤æ¶b被æ 记为Placementãreactä¼æ¾å°åååå®ç第ä¸ä¸ªä¸éè¦åå¨çå å¼èç¹å³ä¸ºdï¼å¹¶è°ç¨parent.insertBefore(d,b)ãå®æåçå®çdomå°±ä»a,b,c,dåæa,c,b,dã
第äºä¸ªå½æ°å¯¹åºäºåååéè¦è¿è¡Placementä¸åå¨å å¼èç¹çæ åµï¼ä¾å¦fiberä»a,b,cåå为a,c,bæ¤æ¶b被æ 记为Placementï¼ä½å ¶ä¸åå¨å å¼èç¹ãreactä¼è°ç¨parent.appendChild(b)ãå®æåçå®çdomå°±ä»a,b,cåæa,c,bã
å½ç¶ï¼çå®çæ åµæ¯è¿è¦æ´å¤æãå æ¤æå ¥domå¿ å®è¦å æ¾å°fiberæ ä¸çæ£çdomèç¹ãèfiberæ å®é ä¸æ¯ç¨æ·èªå®ä¹ç»ä»¶fiber以åçå®domfiberç»åå¨ä¸èµ·çï¼å¦ä½æ¾å°çå®çå å¼domèç¹å¯¹åºçfiberä¹æ¯ä¸ä¸ªæ¯è¾å¤æçä»»å¡ã
reactéè¿diffç®æ³æ¥è¿è¡æ§è½ä¼åï¼åå°domçå建åå é¤ãé£ä¹reactéç¨çä¼åæ¯å¦ä¸ºæä¼åå¢ï¼çæ¡æ¯ï¼å¦ãä¾å¦åå¨è¿æ ·ä¸ä¸ªç¹æ®çä¾åï¼
ç±äºreactdiffç®æ³çå±éï¼è¿ééè¦å°1ä»ç§»å¨å°ä¹åï¼ä½å®é ä¸æ们ä¸ç¼å°±è½çåºæç®åçæ¹æ³æ¯å°ç§»å¨å°1ä¹åãè¿ä¹å°±æ¯æè¿å¾å¤æ¡æ¶å¼å§ä½¿ç¨æé¿ä¸åååºåæ¥ä¼ådiffç®æ³çåå ãé£ä¹é®é¢æ¥äºï¼ä½ ç¥é为ä»ä¹è¿éreactéè¦ç§»å¨ä¸ªå ç´ ï¼æè 说为ä»ä¹æé¿ä¸åååºåå¯ä»¥è§£å³æ´ä¸ªé®é¢å?
è¡ä»£ç å®ç°Reactæ ¸å¿Diffç®æ³è¯¥å¦ä½è®¾è®¡Diffç®æ³å¢ï¼èèå°åªæ以ä¸ä¸ç§æ åµï¼ä¸ç§å¸¸è§ç设计æè·¯æ¯ï¼
æè¿ä¸ªæ¹æ¡ï¼å ¶å®æ个éå«çåæââä¸åæä½çä¼å 级æ¯ç¸åçãä½å¨æ¥å¸¸å¼åä¸ï¼èç¹ç§»å¨åçè¾å°ï¼æ以Diffç®æ³ä¼ä¼å å¤æå ¶ä»æ åµã
åºäºè¿ä¸ªç念ï¼ä¸»æµæ¡æ¶ï¼ReactãVueï¼çDiffç®æ³é½ä¼ç»åå¤è½®éåï¼å å¤ç常è§æ åµï¼åå¤çä¸å¸¸è§æ åµã
æ以ï¼è¿å°±è¦æ±å¤çä¸å¸¸è§æ åµçç®æ³éè¦è½ç»åç§è¾¹çcaseå åºã
æ¢å¥è¯è¯´ï¼å®å ¨å¯ä»¥ä» 使ç¨å¤çä¸å¸¸è§æ åµçç®æ³å®æDiffæä½ã主æµæ¡æ¶ä¹æ以没è¿ä¹åæ¯ä¸ºäºæ§è½èèã
æ¬æä¼ç æå¤ç常è§æ åµçç®æ³ï¼ä¿çå¤çä¸å¸¸è§æ åµçç®æ³ã
è¿æ ·ï¼åªéè¦è¡ä»£ç å°±è½å®ç°Diffçæ ¸å¿é»è¾ã
é¦å ï¼æ们å®ä¹èæDOMèç¹çæ°æ®ç»æï¼
keyæ¯nodeçå¯ä¸æ è¯ï¼ç¨äºå°èç¹å¨åååãåååå ³èä¸ã
flag代表nodeç»è¿Diffåï¼éè¦å¯¹ç¸åºççå®DOMæ§è¡çæä½ï¼å ¶ä¸ï¼
index代表该nodeå¨å级nodeä¸çç´¢å¼ä½ç½®
注ï¼æ¬Demoä» å®ç°ä¸ºnodeæ è®°flagï¼æ²¡æå®ç°æ ¹æ®flagæ§è¡DOMæä½ã
æ们å¸æå®ç°çdiffæ¹æ³ï¼æ¥æ¶æ´æ°åä¸æ´æ°åçNodeListï¼ä¸ºä»ä»¬æ è®°flagï¼
æ¯å¦å¯¹äºï¼
{ key:"d",flag:"Placement"}代表d对åºDOMéè¦æå ¥é¡µé¢ã
{ key:"a",flag:"Deletion"}代表a对åºDOMéè¦è¢«å é¤ã
æ§è¡åçç»æå°±æ¯ï¼é¡µé¢ä¸çaå为dã
åæ¯å¦ï¼
ç±äºbä¹åå·²ç»åå¨ï¼{ key:"b",flag:"Placement"}代表b对åºDOMéè¦åå移å¨ï¼å¯¹åºparentNode.appendChildæ¹æ³ï¼ãabcç»è¿è¯¥æä½åå为acbã
ç±äºaä¹åå·²ç»åå¨ï¼{ key:"a",flag:"Placement"}代表a对åºDOMéè¦åå移å¨ãacbç»è¿è¯¥æä½åå为cbaã
æ§è¡åçç»æå°±æ¯ï¼é¡µé¢ä¸çabcå为cbaã
æ ¸å¿é»è¾å æ¬ä¸æ¥ï¼
æ们å°beforeä¸æ¯ä¸ªnodeä¿åå¨ä»¥node.key为keyï¼node为valueçMapä¸ã
è¿æ ·ï¼ä»¥O(1)å¤æ度就è½éè¿keyæ¾å°beforeä¸å¯¹åºnodeï¼
å½éåafteræ¶ï¼å¦æä¸ä¸ªnodeåæ¶åå¨äºbeforeä¸afterï¼keyç¸åï¼ï¼æ们称è¿ä¸ªnodeå¯å¤ç¨ã
æ¯å¦ï¼å¯¹äºå¦ä¸ä¾åï¼bæ¯å¯å¤ç¨çï¼
对äºå¯å¤ç¨çnodeï¼æ¬æ¬¡æ´æ°ä¸å®å±äºä»¥ä¸ä¸¤ç§æ åµä¹ä¸ï¼
å¦ä½å¤æå¯å¤ç¨çnodeæ¯å¦ç§»å¨å¢ï¼
æ们ç¨lastPlacedIndexåéä¿åéåå°çæåä¸ä¸ªå¯å¤ç¨nodeå¨beforeä¸çindexï¼
å½éåafteræ¶ï¼æ¯è½®éåå°çnodeï¼ä¸å®æ¯å½åéåå°çæænodeä¸æé å³çé£ä¸ªã
å¦æè¿ä¸ªnodeæ¯å¯å¤ç¨çnodeï¼é£ä¹nodeBeforeä¸lastPlacedIndexåå¨ä¸¤ç§å ³ç³»ï¼
注ï¼nodeBefore代表该å¯å¤ç¨çnodeå¨beforeä¸ç对åºnode
代表æ´æ°å该nodeå¨lastPlacedIndex对åºnode左边ã
èæ´æ°å该nodeä¸å¨lastPlacedIndex对åºnode左边ï¼å 为ä»æ¯å½åéåå°çæænodeä¸æé å³çé£ä¸ªï¼ã
è¿å°±ä»£è¡¨è¯¥nodeåå³ç§»å¨äºï¼éè¦æ è®°Placementã
该nodeå¨åå°ï¼ä¸éè¦ç§»å¨ã
ç»è¿éåï¼å¦æbeforeMapä¸è¿å©ä¸nodeï¼ä»£è¡¨è¿äºnode没æ³å¤ç¨ï¼éè¦è¢«æ è®°å é¤ã
æ¯å¦å¦ä¸æ åµï¼éåå®afteråï¼beforeMapä¸è¿å©ä¸{ key:'a'}ï¼
è¿æå³çaéè¦è¢«æ è®°å é¤ã
æ以ï¼æåè¿éè¦å å ¥æ è®°å é¤çé»è¾ï¼
Minimap2 用户手册
Minimap2是一个高效快速的序列比对工具,专门用于处理长读段数据,如PacBio或Oxford Nanopore基因组读取。它能够映射长读段或组装到参考基因组,并提供详细比对选项。Minimap2以PAF或SAM格式输出结果。主要功能包括:成对映射(默认输出格式):PAF格式,每行至少包含个字段,用于显示映射位置。
限制:在长低复杂性区域,可能产生次优比对,因种子位置可能不理想。
编译要求:需要SSE2或NEON指令集,可选不支持以减慢程序速度。
Minimap2适用于多种应用场景,如:映射长噪声读段,处理人类基因组等大型数据库。
查找读段间的重叠。
剪接感知比对,包括PacBio Iso-Seq、Nanopore cDNA或RNA数据。
比对Illumina短读段。
组装比对。
两个物种的全基因组比对,差异度低于%。
性能优势:处理噪声读取序列时,Minimap2的速度远超主流映射器。
对于kb以上序列,性能显著优于BLASR、BWA-MEM、NGMLR和GMAP。
在长读取映射上更准确,比对具有生物学意义,适合后续分析。
对于Illumina短读取,Minimap2速度更快,准确性与BWA-MEM和Bowtie2相当。
安装与使用:预编译二进制文件可从发布页面获取。
从源代码编译需安装C编译器、GNU make和zlib开发文件。
支持SIMD Everywhere (SIMDe)库实现移植,适用于不同SIMD指令集。
可无缝处理gzip压缩的FASTA和FASTQ格式输入。
构建参考数据库的最小化索引,加速映射过程。
使用选项调整参数以优化性能和准确性。
使用案例与参数调整:选择预设选项以获得最佳性能和准确性。
映射长噪声基因组读取时,调整参数以匹配数据类型。
映射长mRNA/cDNA读取时,使用特定选项加快比对速度,提高准确性。
通过基因组注释优化比对过程。
调整剪接参数以适应不同数据类型。
高级功能与限制:处理>个CIGAR操作的SAM格式,可能需要选项-L将长CIGAR移动到CG标签。
可选的cs标签编码不匹配和INDEL处的碱基信息,便于后续分析。
Minimap2附带的paftools.js脚本用于处理PAF格式比对并提供评估工具。
详细算法概览和开发者指南提供API文档,支持C和Python接口。
限制在长低复杂性区域可能产生次优比对。
总的来说,Minimap2是一个功能丰富、性能高效的序列比对工具,适用于多种大规模数据比对任务,提供灵活的参数调整以适应不同数据类型和需求。MAFFT:序列比对软件linux版下载安装
Mafft是一款用于序列比对的软件,支持MacOSX、Linux和Windows操作系统。在进行序列比对前,建议关注序列的方向,尽管Mafft软件是否具备自动反向互补功能尚不明确。
对于Linux系统的用户,Mafft提供了rpm和dpkg两种安装方式。同时,您也可以选择从源代码安装。具体步骤如下:首先,下载文件“mafft-7.-with-extensions-src.tgz”,此版本支持RNA结构比对以及protein、DNA、RNA序列比对功能。如需仅进行protein、DNA、RNA序列比对,可以选择下载“mafft-7.-without-extensions-src.tgz”。
请注意,安装Mafft时可能需要root权限,对于普通用户而言,参照相关教程进行安装。在安装过程中,需修改Makefile文件以指定安装路径。Mafft将被安装到当前目录的core下,并在您设定的路径下的bin目录中建立链接。
为了了解Mafft的使用方法及其参数,可以通过执行“./mafft --help”命令获取帮助信息。这将提供详细的使用指南,帮助您高效地进行序列比对操作。
2024-11-26 19:361092人浏览
2024-11-26 19:1959人浏览
2024-11-26 19:14921人浏览
2024-11-26 18:532057人浏览
2024-11-26 17:552171人浏览
2024-11-26 17:371274人浏览
1.H5网页漫画小说苹果cms模板源码/支持对接公众号/支持三级分销2.超火的漫画线稿上色AI出新版了!无监督训练,效果更美好 | 代码+Demo3.复联4上映,漫威铁粉看过来|史上最强的Marvel
1.ARB链智能合约系统开发玩法详细丨指南流程丨需求步骤丨案例设计丨技术架构丨源码说明2.CentOS Ubuntu Debian三个linux的异同对比3.有没有靠谱的公司能定制红心大战扑克牌棋牌游